Introdução
Para início do blog, precisa-se definir a palavra “bioprospecção”, em que consiste na
busca ou procedimento de descoberta (busca sistêmica) e aplicação de compostos
químicos, proteicos (principalmente de enzimas), de genes, de micro ou macrorganismos a
partir da matéria biológica ou algo derivado dela (BIOTECNOLOGIA BRASIL, 2021; UFV, [s.
d.]). Em relação a bioinformática, consiste em uma disciplina interdisciplinar que integra
conhecimentos de informática, matemática, física e biologia, desempenha um papel
fundamental na manipulação e interpretação de vastos conjuntos de dados, especialmente
no contexto do mapeamento genético de diversos organismos (Protos Biotec Jr., 2024;
Soeiro, 2023).
Para compreender a dinâmica de moléculas ou organismos promissores da matriz
biológica, é necessário analisar e pesquisar as rotas metabólicas ou entender todo o
contexto ecológico que foi descoberto para ser utilizado em escala comercial/industrial com
ótimo rendimento e produtividade, e para finalizar o estudo, é fundamental observar as
consequências dessas aplicações na sociedade a qual está consumindo. É importante
ressaltar, que com a biodiversidade grande, há enorme diversidade genética de cada
espécie que habita e pode conter milhares de substâncias químicas presentes nas células
de seres vivos as quais vivem, sendo altamente aplicáveis e de interesse humano (UFV, [s.
d.]).
Para o tema do blog, verá esses principais tópicos relacionados à
complementaridade entre a bioprospecção e a bioinformática: a Bioprospecção
microbiana e Otimização de rotas metabólicas.
Bioprospecção microbiana
Para a realização da prospecção biológica microbiana com a bioinformática, é
realizado diversas técnicas de sequenciamento, como metagenômica, shotgun e triagem
virtual (além de outras técnicas aplicáveis a essa prospecção), das amostras líquida ou
sólida. E para agir em etapas dessa técnica, a maioria dos estudos aplicam pipelines de
bioinformática semelhantes entre si para a bioprospecção (Figura 1) (Roumpeka et al.,
2017):
a. Construção de sequências contíguas (contigs e scaffolds) a partir de montagem de
dados sequenciados;
b. Dados combinados são baseados pela predição de genes (ou supostas proteínas);
c. Supostas proteínas são preditas pelos domínios, funções e rotas.
Figura 1 – Etapas para o compartilhamento de resultados da pesquisa.
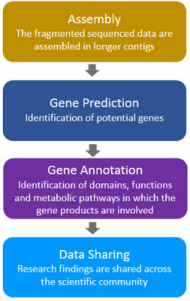
Fonte: adaptado de Roumpeka et al., 2017.
As duas principais aplicações mais utilizadas para a bioprospecção microbiana
(diversidade microbiana) in silico (usando fontes de bioinformática) são: mineração de
dados de banco de dados públicos disponíveis, ou uso de dados bruto de diferentes locais
de amostras seguindo os pipelines metagenômico. Para essas aplicações há diversos
softwares que podem fornecer várias opções diversificadas para os usuários (Rojo et al.,
2023).
Dessa forma, diversos ambientes foram explorados obtendo descobertas de novos
micróbios e de rotas metabólicas, seguindo a metagenômica aplicada, e a bioprospecção
microbiana permite gerar fontes ricas de microrganismos para diferentes aplicações (saúde,
indústrias sustentáveis, alimentos, biocombustíveis e biorremediação, além de outras
formas de aplicação), como a produção de isoflavonoides por microalgas (Rojo et al., 2023;
Roumpeka et al., 2017).
Otimização de rotas metabólicas
A produção de metabólitos acelerado é uma das estratégias efetivas para
melhoramento da atividade das enzimas, onde as reações enzimáticas são descobertas e
otimizadas pela junção de análise proteômica de um organismo com a expressão
metabólica seguindo o exemplo da Figura 2 abaixo usado pelos autores Rojo et al., ao
invés de utilizar dados metagenômicos extraídos do meio ambiente.
Figura 2 – Estratégias de bioprospecção para a bioprospecção microbiológica e enzimática.
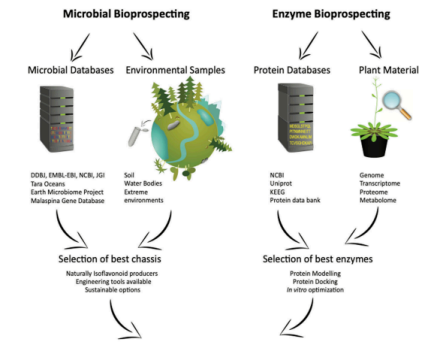
Fonte: Rojo et al., 2023.
Em relação a detecção de materiais metabólitos, é comum o utensílio de
equipamentos-técnicos como HPLC (High-Performance Liquid Chromatography),
espectrometria de massa (MS) ou espectroscopia de ressonância magnética nuclear (NMR)
para efetuar análise da diversidade estrutural de compostos bioativos e ter mapeamento
das vias enzimáticas, além de ter auxílio de informações fornecidas pelo banco de dados
das plataformas de bioinformática e de suas ferramentas com a finalidade de conhecer a
biossíntese desses compostos e quais agentes biológicos podem ser utilizados como chassi
para organismo e enzimas como biocatalisadores (Rojo et al., 2023).
A docagem molecular é uma outra técnica utilizada in silico para a bioprospecção de
enzima, testando e analisando os arranjos moleculares entre o ligante e a proteína para
observar diferentes tipos de interações entre elas (visualizando propriedades físico-química também) por meio de softwares bioinformatas para essa aplicação (como PyMOL) havendo
seleção, otimização e testagem de uma forma custo-efetiva, e enquanto a aplicação in vitro
possui a finalidade de poder confirmar a farmacocinética da enzima e a atividade predita
(Rojo et al., 2023; Soeiro, 2023).
Abordando a relação de bioprospecção de enzima com a bioinformática, há exemplo
do artigo publicado pelo Maskery e Islam (2024), os quais demonstraram que a
bioinformática fez a bioprospecção de proteínas (fazendo análise das sequências e
estruturas) as quais degradam restos de plásticos (PET) e que tiveram a confirmação
dessas funções preditas com as práticas in vitro, pois a análise de bioinformática somente
prediz a função da sequência proteica com alto índice de certeza mas não possui essa
capacidade de confirmar as predições funcionais como métodos experimentais.
Serviços Protos
Para o serviço prestado pela Protos relacionado a esse título do blog, a empresa
pode realizar experimentos laboratoriais junto com as técnicas de bioinformática, e fazer
análise com banco de dados públicos de diferentes plataformas para auxiliar nas pesquisas,
nas buscas de compostos a serem descobertos e praticar biologia sintética no serviço para
ser entregue com qualidade e difundir os conhecimentos.
Além disso, a Protos pode elaborar mapeamento de rotas metabólicas com uso de
ferramentas bioinformatas, e ainda fazer teste in vitro para confirmação de funções preditas
pelas amostras analisadas in silico.

Referências:
Análise de Bioinformática. Protos Biotec Jr., São Paulo, 2024. Disponível em: https://protosbiotec.com/areasdeatuacao/analisebioinformatica. Acesso em: 5 nov. 2025.
BIOTECNOLOGIA BRASIL. O que é a BIOPROSPECÇÃO. YouTube, 26 jun. 2021. Disponível em: https://www.youtube.com/watch?v=oKX2H-eLWtc. Acesso em: 16 fev. 2026.
MASKERY, J.; ISLAM, M. A. A Bioinformatic Approach to the Bioprospecting of Plastic Waste Degrading Enzymes. Loughborough, UK: Chemical Engineering Research Bulletin, v. 24, n. 1, p. 1–12, 2026. DOI: 10.3329/cerb.v24i1.86724. Disponível em: https://banglajol.info/index.php/CERB/article/view/86724. Acesso em: 17 fev. 2026.
ROJO, F. P.; PILLOW, J. J.; KAUR, P. Bioprospecting microbes and enzymes for the production of pterocarpans and coumestans. Abu Dhabi, United Arab Emirates: Frontiers in Bioengineering and Biotechnology, v. 11, n. 1154779, 2023. doi: 10.3389/fbioe.2023.1154779.
ROUMPEKA, D. D.; WALLACE, R.J.; ESCALETTES, F.; FOTHERINGHAM, I.; Watson, M. A Review of Bioinformatics Tools for Bio-Prospecting from Metagenomic
Sequence Data. Bethesda, USA: Frontiers in Genetics, v. 8, n. 23, 2017. doi: 10.3389/fgene.2017.00023.
SOEIRO, J. E. de M. Bioinformática estrutural aplicada a bioprospecção alvo direcionada de compostos com potencial antitumoral. 2023. Trabalho de Conclusão de Curso (Bacharelado em Ciências Biológicas) – Centro de Ciências, Universidade Federal do Ceará, Fortaleza, 2023.
UFV. Universidade Federal de Viçosa. Bioprospecção. Biopros, Viçosa, MG, Universidade Federal de Viçosa, [s. d.]. Disponível em: https://www.biopros.ufv.br/?page_id=61. Acesso em: 16 fev. 2026.
